تحسين تصنيف الميزات باستخدام نوى الكم المسقطة
تقدير الاستخدام: 80 دقيقة على معالج Heron r3 (ملاحظة: هذا تقدير فحسب. قد يختلف وقت التشغيل الفعلي لديك.)
في هذا الدرس التعليمي، نستعرض كيفية تشغيل نواة الكم المسقطة (PQK) مع Qiskit على مجموعة بيانات بيولوجية من العالم الحقيقي، استناداً إلى الورقة البحثية Enhanced Prediction of CAR T-Cell Cytotoxicity with Quantum-Kernel Methods [1].
PQK هي طريقة تُستخدم في التعلم الآلي الكمومي (QML) لترميز البيانات الكلاسيكية في فضاء الميزات الكمومي وإسقاطها مجدداً إلى المجال الكلاسيكي، وذلك باستخدام الحواسيب الكمومية لتعزيز اختيار الميزات. تتضمن هذه الطريقة ترميز البيانات الكلاسيكية في حالات كمومية باستخدام دائرة كمومية، وعادةً من خلال عملية تُسمى رسم خريطة الميزات، حيث تُحوَّل البيانات إلى فضاء هيلبرت عالي الأبعاد. يشير الجانب "المسقط" إلى استخلاص المعلومات الكلاسيكية من الحالات الكمومية عبر قياس مُراقَبات محددة، من أجل بناء مصفوفة نواة يمكن استخدامها في خوارزميات النواة الكلاسيكية كآلات المتجهات الداعمة. يستفيد هذا النهج من المزايا الحسابية للأنظمة الكمومية لتحقيق أداء أفضل محتمل في مهام معينة مقارنةً بالطرق الكلاسيكية.
يفترض هذا الدرس التعليمي أيضاً إلماماً عاماً بأساليب QML. لمزيد من الاستكشاف في مجال QML، يمكن الرجوع إلى دورة التعلم الآلي الكمومي في IBM Quantum Learning.
المتطلبات
قبل البدء في هذا الدرس التعليمي، تأكد من تثبيت ما يلي:
- Qiskit SDK الإصدار 2.0 أو أحدث، مع دعم التصور
- Qiskit Runtime الإصدار 0.40 أو أحدث (
pip install qiskit-ibm-runtime) - Category encoders 2.8.1 (
pip install category-encoders) - NumPy 2.3.2 (
pip install numpy) - Pandas 2.3.2 (
pip install pandas) - Scikit-learn 1.7.1 (
pip install scikit-learn) - Tqdm 4.67.1 (
pip install tqdm)
الإعداد
# Added by doQumentation — required packages for this notebook
!pip install -q category-encoders numpy pandas qiskit qiskit-ibm-runtime scipy scikit-learn tqdm
import warnings
# Standard libraries
import os
import numpy as np
import pandas as pd
# Machine learning and data processing
import category_encoders as ce
from scipy.linalg import inv, sqrtm
from sklearn.metrics.pairwise import rbf_kernel
from sklearn.model_selection import GridSearchCV, StratifiedKFold
from sklearn.svm import SVC
# Qiskit and Qiskit Runtime
from qiskit import QuantumCircuit
from qiskit.circuit import ParameterVector
from qiskit.circuit.library import UnitaryGate, ZZFeatureMap
from qiskit.quantum_info import SparsePauliOp, random_unitary
from qiskit.transpiler import generate_preset_pass_manager
from qiskit_ibm_runtime import (
Batch,
EstimatorOptions,
EstimatorV2 as Estimator,
QiskitRuntimeService,
)
# Progress bar
import tqdm
warnings.filterwarnings("ignore")
الخطوة 1: تعيين المدخلات الكلاسيكية إلى مسألة كمومية
تحضير مجموعة البيانات
في هذا الدرس التعليمي نستخدم مجموعة بيانات بيولوجية من العالم الحقيقي لمهمة تصنيف ثنائي، تم توليدها بواسطة Daniels et al. (2022) ويمكن تنزيلها من المواد التكميلية المرفقة بالورقة البحثية. تتألف البيانات من خلايا CAR T، وهي خلايا T مهندسة وراثياً تُستخدم في العلاج المناعي لعلاج أنواع معينة من السرطان. يتم تعديل خلايا T، وهي نوع من خلايا المناعة، في المختبر لتعبّر عن مستقبلات المستضد الخيمري (CARs) التي تستهدف بروتينات محددة على الخلايا السرطانية. يمكن لخلايا T المعدَّلة هذه التعرف على الخلايا السرطانية وتدميرها بفاعلية أكبر. ميزات البيانات هي بنيات خلايا CAR T، التي تشير إلى المكوّن البنيوي أو الوظيفي المحدد للـ CAR المهندَس في خلايا T. بناءً على هذه البنيات، تتمثل مهمتنا في التنبؤ بسُمِّية خلية CAR T المعطاة، وتصنيفها إما كسامة أو غير سامة. يوضح ما يلي الدوال المساعدة لمعالجة هذه المجموعة من البيانات.
def preprocess_data(dir_root, args):
"""
Preprocess the training and test data.
"""
# Read from the csv files
train_data = pd.read_csv(
os.path.join(dir_root, args["file_train_data"]),
encoding="unicode_escape",
sep=",",
)
test_data = pd.read_csv(
os.path.join(dir_root, args["file_test_data"]),
encoding="unicode_escape",
sep=",",
)
# Fix the last motif ID
train_data[train_data == 17] = 14
train_data.columns = [
"Cell Number",
"motif",
"motif.1",
"motif.2",
"motif.3",
"motif.4",
"Nalm 6 Cytotoxicity",
]
test_data[test_data == 17] = 14
test_data.columns = [
"Cell Number",
"motif",
"motif.1",
"motif.2",
"motif.3",
"motif.4",
"Nalm 6 Cytotoxicity",
]
# Adjust motif at the third position
if args["filter_for_spacer_motif_third_position"]:
train_data = train_data[
(train_data["motif.2"] == 14) | (train_data["motif.2"] == 0)
]
test_data = test_data[
(test_data["motif.2"] == 14) | (test_data["motif.2"] == 0)
]
train_data = train_data[
args["motifs_to_use"] + [args["label_name"], "Cell Number"]
]
test_data = test_data[
args["motifs_to_use"] + [args["label_name"], "Cell Number"]
]
# Adjust motif at the last position
if not args["allow_spacer_motif_last_position"]:
last_motif = args["motifs_to_use"][len(args["motifs_to_use"]) - 1]
train_data = train_data[
(train_data[last_motif] != 14) & (train_data[last_motif] != 0)
]
test_data = test_data[
(test_data[last_motif] != 14) & (test_data[last_motif] != 0)
]
# Get the labels
train_labels = np.array(train_data[args["label_name"]])
test_labels = np.array(test_data[args["label_name"]])
# For the classification task use the threshold to binarize labels
train_labels[train_labels > args["label_binarization_threshold"]] = 1
train_labels[train_labels < 1] = args["min_label_value"]
test_labels[test_labels > args["label_binarization_threshold"]] = 1
test_labels[test_labels < 1] = args["min_label_value"]
# Reduce data to just the motifs of interest
train_data = train_data[args["motifs_to_use"]]
test_data = test_data[args["motifs_to_use"]]
# Get the class and motif counts
min_class = np.min(np.unique(np.concatenate([train_data, test_data])))
max_class = np.max(np.unique(np.concatenate([train_data, test_data])))
num_class = max_class - min_class + 1
num_motifs = len(args["motifs_to_use"])
print(str(max_class) + ":" + str(min_class) + ":" + str(num_class))
train_data = train_data - min_class
test_data = test_data - min_class
return (
train_data,
test_data,
train_labels,
test_labels,
num_class,
num_motifs,
)
def data_encoder(args, train_data, test_data, num_class, num_motifs):
"""
Use one-hot or binary encoding for classical data representation.
"""
if args["encoder"] == "one-hot":
# Transform to one-hot encoding
train_data = np.eye(num_class)[train_data]
test_data = np.eye(num_class)[test_data]
train_data = train_data.reshape(
train_data.shape[0], train_data.shape[1] * train_data.shape[2]
)
test_data = test_data.reshape(
test_data.shape[0], test_data.shape[1] * test_data.shape[2]
)
elif args["encoder"] == "binary":
# Transform to binary encoding
encoder = ce.BinaryEncoder()
base_array = np.unique(np.concatenate([train_data, test_data]))
base = pd.DataFrame(base_array).astype("category")
base.columns = ["motif"]
for motif_name in args["motifs_to_use"][1:]:
base[motif_name] = base.loc[:, "motif"]
encoder.fit(base)
train_data = encoder.transform(train_data.astype("category"))
test_data = encoder.transform(test_data.astype("category"))
train_data = np.reshape(
train_data.values, (train_data.shape[0], num_motifs, -1)
)
test_data = np.reshape(
test_data.values, (test_data.shape[0], num_motifs, -1)
)
train_data = train_data.reshape(
train_data.shape[0], train_data.shape[1] * train_data.shape[2]
)
test_data = test_data.reshape(
test_data.shape[0], test_data.shape[1] * test_data.shape[2]
)
else:
raise ValueError("Invalid encoding type.")
return train_data, test_data
يمكنك تشغيل هذا الدرس التعليمي بتنفيذ الخلية التالية، التي تنشئ تلقائياً هيكل المجلدات المطلوب وتنزّل كلاً من ملفَي التدريب والاختبار مباشرةً في بيئتك. إذا كانت هذه الملفات موجودة لديك محلياً، فستقوم هذه الخطوة بالكتابة فوقها بأمان لضمان توافق الإصدارات.
## Download dataset
# Create data directory if it doesn't exist
!mkdir -p data_tutorial/pqk
# Download the training and test sets from the official Qiskit documentation repo
!wget -q --show-progress -O data_tutorial/pqk/train_data.csv \
https://raw.githubusercontent.com/Qiskit/documentation/main/datasets/tutorials/pqk/train_data.csv
!wget -q --show-progress -O data_tutorial/pqk/test_data.csv \
https://raw.githubusercontent.com/Qiskit/documentation/main/datasets/tutorials/pqk/test_data.csv
!wget -q --show-progress -O data_tutorial/pqk/projections_train.csv \
https://raw.githubusercontent.com/Qiskit/documentation/main/datasets/tutorials/pqk/projections_train.csv
!wget -q --show-progress -O data_tutorial/pqk/projections_test.csv \
https://raw.githubusercontent.com/Qiskit/documentation/main/datasets/tutorials/pqk/projections_test.csv
# Check the files have been downloaded
!echo "Dataset files downloaded:"
!ls -lh data_tutorial/pqk/*.csv
args = {
"file_train_data": "train_data.csv",
"file_test_data": "test_data.csv",
"motifs_to_use": ["motif", "motif.1", "motif.2", "motif.3"],
"label_name": "Nalm 6 Cytotoxicity",
"label_binarization_threshold": 0.62,
"filter_for_spacer_motif_third_position": False,
"allow_spacer_motif_last_position": True,
"min_label_value": -1,
"encoder": "one-hot",
}
dir_root = "./"
# Preprocess data
train_data, test_data, train_labels, test_labels, num_class, num_motifs = (
preprocess_data(dir_root=dir_root, args=args)
)
# Encode the data
train_data, test_data = data_encoder(
args, train_data, test_data, num_class, num_motifs
)
14:0:15
نُحوِّل أيضاً مجموعة البيانات بحيث يُمثَّل على شكل لأغراض التحجيم.
# Change 1 to pi/2
angle = np.pi / 2
tmp = pd.DataFrame(train_data).astype("float64")
tmp[tmp == 1] = angle
train_data = tmp.values
tmp = pd.DataFrame(test_data).astype("float64")
tmp[tmp == 1] = angle
test_data = tmp.values
نتحقق من أحجام وأشكال مجموعتَي بيانات التدريب والاختبار.
print(train_data.shape, train_labels.shape)
print(test_data.shape, test_labels.shape)
(172, 60) (172,)
(74, 60) (74,)
الخطوة 2: تحسين المسألة لتنفيذها على عتاد الكم
الدائرة الكمومية
نبني الآن خريطة الميزات التي تُضمِّن مجموعة بياناتنا الكلاسيكية في فضاء ميزات أعلى الأبعاد. لهذا التضمين، نستخدم ZZFeatureMap من Qiskit.
feature_dimension = train_data.shape[1]
reps = 24
insert_barriers = True
entanglement = "pairwise"
# ZZFeatureMap with linear entanglement and a repetition of 2
embed = ZZFeatureMap(
feature_dimension=feature_dimension,
reps=reps,
entanglement=entanglement,
insert_barriers=insert_barriers,
name="ZZFeatureMap",
)
embed.decompose().draw(output="mpl", style="iqp", fold=-1)

خيار تضمين كمومي آخر هو الـ ansatz الخاص بتطور هاميلتوني هايزنبرغ أحادي البعد. يمكنك تخطي تشغيل هذا القسم إذا أردت الاستمرار باستخدام ZZFeatureMap.
feature_dimension = train_data.shape[1]
num_qubits = feature_dimension + 1
embed2 = QuantumCircuit(num_qubits)
num_trotter_steps = 6
pv_length = feature_dimension * num_trotter_steps
pv = ParameterVector("theta", pv_length)
# Add Haar random single qubit unitary to each qubit as initial state
np.random.seed(42)
seeds_unitary = np.random.randint(0, 100, num_qubits)
for i in range(num_qubits):
rand_gate = UnitaryGate(random_unitary(2, seed=seeds_unitary[i]))
embed2.append(rand_gate, [i])
def trotter_circ(feature_dimension, num_trotter_steps):
num_qubits = feature_dimension + 1
circ = QuantumCircuit(num_qubits)
# Even
for i in range(0, feature_dimension, 2):
circ.rzz(2 * pv[i] / num_trotter_steps, i, i + 1)
for i in range(0, feature_dimension, 2):
circ.rxx(2 * pv[i] / num_trotter_steps, i, i + 1)
for i in range(0, feature_dimension, 2):
circ.ryy(2 * pv[i] / num_trotter_steps, i, i + 1)
# Odd
for i in range(1, feature_dimension, 2):
circ.rzz(2 * pv[i] / num_trotter_steps, i, i + 1)
for i in range(1, feature_dimension, 2):
circ.rxx(2 * pv[i] / num_trotter_steps, i, i + 1)
for i in range(1, feature_dimension, 2):
circ.ryy(2 * pv[i] / num_trotter_steps, i, i + 1)
return circ
# Hamiltonian evolution ansatz
for step in range(num_trotter_steps):
circ = trotter_circ(feature_dimension, num_trotter_steps)
if step % 2 == 0:
embed2 = embed2.compose(circ)
else:
reverse_circ = circ.reverse_ops()
embed2 = embed2.compose(reverse_circ)
embed2.draw(output="mpl", style="iqp", fold=-1)
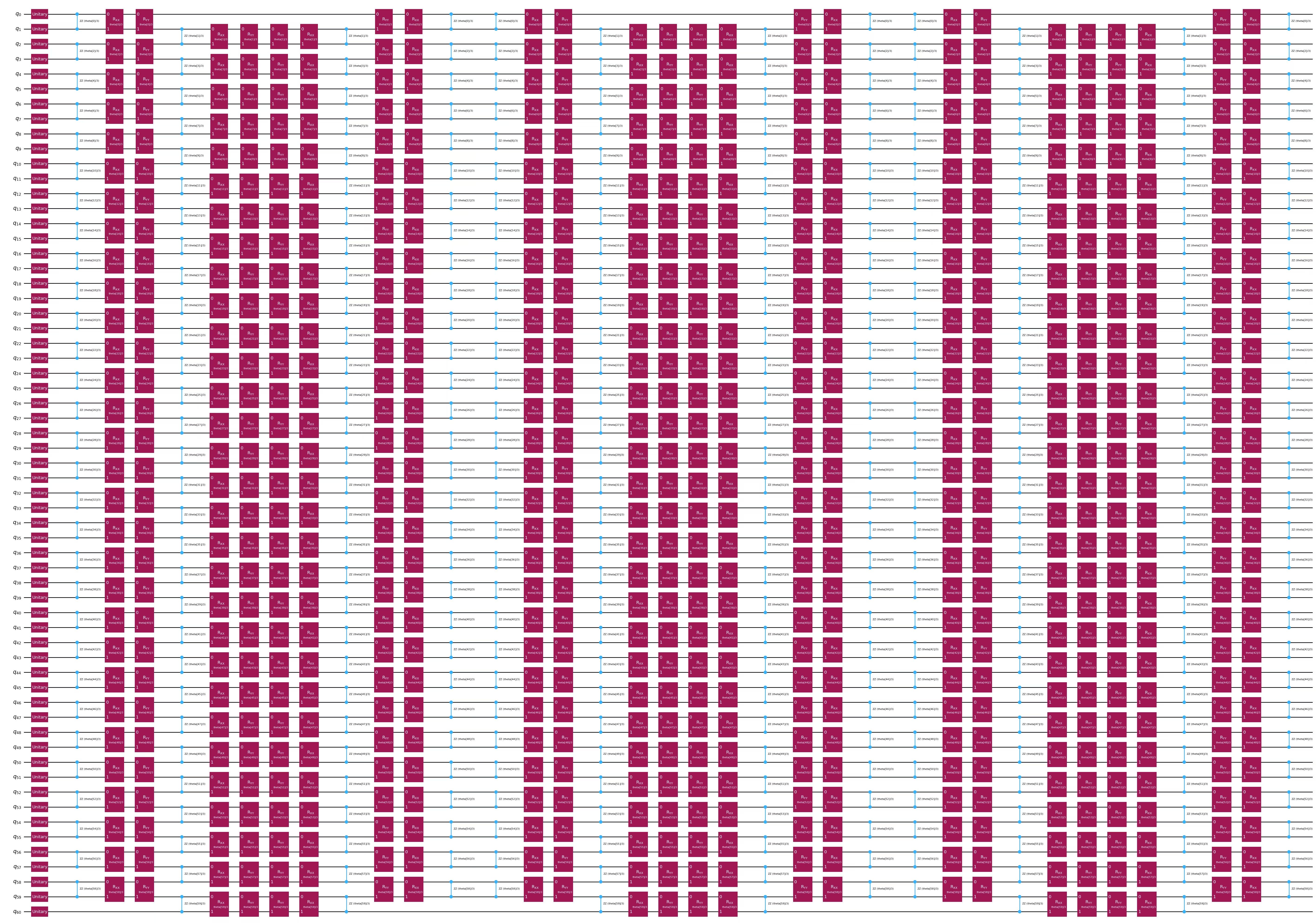
الخطوة 3: التنفيذ باستخدام أوليات Qiskit
قياس مصفوفات الك�ثافة المختزلة أحادية الكيوبت (1-RDMs)
اللبنات الأساسية لنوى الكم المسقطة هي مصفوفات الكثافة المختزلة (RDMs)، التي تُحصَل عليها من خلال القياسات الإسقاطية لخريطة الميزات الكمومية. في هذه الخطوة، نحصل على جميع مصفوفات الكثافة المختزلة أحادية الكيوبت (1-RDMs)، والتي ستُقدَّم لاحقاً إلى دالة النواة الأسية الكلاسيكية.
لنتأمل كيفية حساب 1-RDM لنقطة بيانات واحدة من مجموعة البيانات قبل التشغيل على جميع البيانات. إن 1-RDMs هي مجموعة من قياسات الكيوبت الواحد لعوامل باولي X وY وZ على جميع الكيوبتات. وذلك لأن مصفوفة الكثافة المختزلة لكيوبت واحد يمكن التعبير عنها كاملةً على النحو التالي:
أولاً نختار الخلفية التي سنستخدمها.
service = QiskitRuntimeService()
backend = service.least_busy(
operational=True, simulator=False, min_num_qubits=133
)
target = backend.target
ثم نشغّل الدائرة الكمومية ونقيس الإسقاطات. لاحظ أننا نُفعِّل تخفيف الأخطاء، بما في ذلك استقراء التشويش الصفري (ZNE).
# Let's select the ZZFeatureMap embedding for this example
qc = embed
num_qubits = feature_dimension
# Identity operator on all qubits
id = "I" * num_qubits
# Let's select the first training datapoint as an example
parameters = train_data[0]
# Bind parameter to the circuit and simplify it
qc_bound = qc.assign_parameters(parameters)
transpiler = generate_preset_pass_manager(
optimization_level=3, basis_gates=["u3", "cz"]
)
transpiled_circuit = transpiler.run(qc_bound)
# Transpile for hardware
transpiler = generate_preset_pass_manager(optimization_level=3, target=target)
transpiled_circuit = transpiler.run(transpiled_circuit)
# We group all commuting observables
# These groups are the Pauli X, Y and Z operators on individual qubits
observables_x = [
SparsePauliOp(id[:i] + "X" + id[(i + 1) :]).apply_layout(
transpiled_circuit.layout
)
for i in range(num_qubits)
]
observables_y = [
SparsePauliOp(id[:i] + "Y" + id[(i + 1) :]).apply_layout(
transpiled_circuit.layout
)
for i in range(num_qubits)
]
observables_z = [
SparsePauliOp(id[:i] + "Z" + id[(i + 1) :]).apply_layout(
transpiled_circuit.layout
)
for i in range(num_qubits)
]
# We define the primitive unified blocs (PUBs) consisting of the embedding circuit,
# set of observables and the circuit parameters
pub_x = (transpiled_circuit, observables_x)
pub_y = (transpiled_circuit, observables_y)
pub_z = (transpiled_circuit, observables_z)
# Experiment options for error mitigation
num_randomizations = 300
shots_per_randomization = 100
noise_factors = [1, 3, 5]
experimental_opts = {}
experimental_opts["resilience"] = {
"measure_mitigation": True,
"zne_mitigation": True,
"zne": {
"noise_factors": noise_factors,
"amplifier": "gate_folding",
"extrapolated_noise_factors": [0] + noise_factors,
},
}
experimental_opts["twirling"] = {
"num_randomizations": num_randomizations,
"shots_per_randomization": shots_per_randomization,
"strategy": "active-accum",
}
# We define and run the estimator to obtain <X>, <Y> and <Z> on all qubits
estimator = Estimator(mode=backend, options=experimental_opts)
job = estimator.run([pub_x, pub_y, pub_z])
بعد ذلك نستخرج النتائج.
job_result_x = job.result()[0].data.evs
job_result_y = job.result()[1].data.evs
job_result_z = job.result()[2].data.evs
print(job_result_x)
print(job_result_y)
print(job_result_z)
[ 3.67865951e-03 1.01158571e-02 -3.95790878e-02 6.33984326e-03
1.86035759e-02 -2.91533268e-02 -1.06374793e-01 4.48873518e-18
4.70201764e-02 3.53997968e-02 2.53130819e-02 3.23903401e-02
6.06327843e-03 1.16313667e-02 -1.12387504e-02 -3.18457725e-02
-4.16445718e-04 -1.45609602e-03 -4.21737114e-01 2.83705669e-02
6.91332890e-03 -7.45363001e-02 -1.20139326e-02 -8.85566135e-02
-3.22648394e-02 -3.24228074e-02 6.20431299e-04 3.04225434e-03
5.72795792e-03 1.11288428e-02 1.50395861e-01 9.18380197e-02
1.02553163e-01 2.98312847e-02 -3.30298912e-01 -1.13979648e-01
4.49159340e-03 8.63861493e-02 3.05666566e-02 2.21463145e-04
1.45946735e-02 8.54537275e-03 -8.09805979e-02 -2.92608104e-02
-3.91243644e-02 -3.96632760e-02 -1.41187613e-01 -1.07363243e-01
1.81089440e-02 2.70778895e-02 1.45139414e-02 2.99480458e-02
4.99137134e-02 7.08789852e-02 4.30565759e-02 8.71287156e-02
1.04334798e-01 7.72191962e-02 7.10059720e-02 1.04650403e-01]
[-7.31765102e-05 7.42669174e-03 9.82277344e-03 5.92638249e-02
4.24120486e-02 -9.06473416e-03 4.55057675e-03 8.43494094e-03
6.92097339e-02 -6.82234424e-02 6.13509008e-02 3.94200491e-02
-1.24037979e-02 1.01976642e-01 7.90538600e-03 -7.19726160e-02
-1.19501703e-16 -1.03796614e-02 7.37382463e-02 1.97238568e-01
-3.59250635e-02 -2.67554009e-02 3.55010633e-02 7.68877990e-02
6.50677589e-05 -6.59298767e-03 -1.23719487e-02 -6.41938151e-02
1.95603072e-02 -2.48448551e-02 5.17784810e-02 -5.93767100e-02
3.11897681e-02 -3.91959720e-18 -4.47769148e-03 1.39202197e-01
-6.56387523e-02 -5.85665483e-02 9.52905894e-03 -8.61460731e-02
3.91790656e-02 -1.27544375e-01 1.63712244e-01 3.36816934e-04
2.26230028e-02 -2.45023393e-05 4.95635588e-03 1.44779564e-01
3.71625177e-02 3.65675948e-03 2.83694017e-02 -7.10500602e-02
-1.15467702e-01 6.21712129e-03 -4.80958959e-02 2.21021066e-02
7.99062499e-02 -1.87164076e-02 -3.67100369e-02 -2.38923731e-02]
[ 6.85871605e-01 5.07725024e-01 8.71024642e-03 3.34823455e-02
4.58684961e-02 9.44384189e-17 -4.46829296e-02 -2.91296778e-02
4.15466461e-02 2.89628330e-02 1.88624017e-03 5.37110446e-02
2.59579053e-03 1.39327071e-02 -2.90781778e-02 5.07209866e-03
5.83403000e-02 2.60764440e-02 4.45999706e-17 -6.66701417e-03
3.03215873e-01 2.26172533e-02 2.43105960e-02 4.98861041e-18
-2.45530791e-02 6.26940708e-02 1.21058073e-02 2.76675948e-04
2.63980996e-02 2.58302364e-02 7.47856723e-02 8.42728943e-02
5.70989097e-02 6.92955086e-02 -5.68313712e-03 1.32199452e-01
8.90511238e-02 -3.45204621e-02 -1.05445836e-01 6.03864150e-03
2.16291384e-02 8.22303162e-03 1.00856715e-02 6.28973151e-02
6.26727169e-02 6.15399206e-02 9.67320897e-02 1.03045269e-16
1.79688783e-01 -1.59960520e-02 -1.15422952e-02 9.60200470e-03
6.58396672e-02 7.78329830e-03 6.53226955e-02 2.45778685e-03
4.36694753e-03 5.75098762e-03 -2.48896201e-02 8.33740755e-05]
نطبع الآن حجم الدائرة وعمق البوابات ثنائية الكيوبت.
print(f"qubits: {qc.num_qubits}")
print(
f"2q-depth: {transpiled_circuit.depth(lambda x: x.operation.num_qubits==2)}"
)
print(
f"2q-size: {transpiled_circuit.size(lambda x: x.operation.num_qubits==2)}"
)
print(f"Operator counts: {transpiled_circuit.count_ops()}")
transpiled_circuit.draw("mpl", fold=-1, style="clifford", idle_wires=False)
qubits: 60
2q-depth: 64
2q-size: 1888
Operator counts: OrderedDict({'rz': 6016, 'sx': 4576, 'cz': 1888, 'x': 896, 'barrier': 31})

يمكننا الآن التكرار على مجموعة بيانات التدريب بأكملها للحصول على جميع 1-RDMs.
نُوفِّر أيضاً النتائج من تجربة أجريناها على عتاد الكم. يمكنك إما تشغيل التدريب بنفسك عبر تعيين الراية أدناه إلى True، أو استخدام نتائج الإسقاط التي نُوفِّرها.
# Set this to True if you want to run the training on hardware
run_experiment = False
# Identity operator on all qubits
id = "I" * num_qubits
# projections_train[i][j][k] will be the expectation value of the j-th Pauli operator (0: X, 1: Y, 2: Z)
# of datapoint i on qubit k
projections_train = []
jobs_train = []
# Experiment options for error mitigation
num_randomizations = 300
shots_per_randomization = 100
noise_factors = [1, 3, 5]
experimental_opts = {}
experimental_opts["resilience"] = {
"measure_mitigation": True,
"zne_mitigation": True,
"zne": {
"noise_factors": noise_factors,
"amplifier": "gate_folding",
"return_all_extrapolated": True,
"return_unextrapolated": True,
"extrapolated_noise_factors": [0] + noise_factors,
},
}
experimental_opts["twirling"] = {
"num_randomizations": num_randomizations,
"shots_per_randomization": shots_per_randomization,
"strategy": "active-accum",
}
options = EstimatorOptions(experimental=experimental_opts)
if run_experiment:
with Batch(backend=backend):
for i in tqdm.tqdm(
range(len(train_data)), desc="Training data progress"
):
# Get training sample
parameters = train_data[i]
# Bind parameter to the circuit and simplify it
qc_bound = qc.assign_parameters(parameters)
transpiler = generate_preset_pass_manager(
optimization_level=3, basis_gates=["u3", "cz"]
)
transpiled_circuit = transpiler.run(qc_bound)
# Transpile for hardware
transpiler = generate_preset_pass_manager(
optimization_level=3, target=target
)
transpiled_circuit = transpiler.run(transpiled_circuit)
# We group all commuting observables
# These groups are the Pauli X, Y and Z operators on individual qubits
observables_x = [
SparsePauliOp(id[:i] + "X" + id[(i + 1) :]).apply_layout(
transpiled_circuit.layout
)
for i in range(num_qubits)
]
observables_y = [
SparsePauliOp(id[:i] + "Y" + id[(i + 1) :]).apply_layout(
transpiled_circuit.layout
)
for i in range(num_qubits)
]
observables_z = [
SparsePauliOp(id[:i] + "Z" + id[(i + 1) :]).apply_layout(
transpiled_circuit.layout
)
for i in range(num_qubits)
]
# We define the primitive unified blocs (PUBs) consisting of the embedding circuit,
# set of observables and the circuit parameters
pub_x = (transpiled_circuit, observables_x)
pub_y = (transpiled_circuit, observables_y)
pub_z = (transpiled_circuit, observables_z)
# We define and run the estimator to obtain <X>, <Y> and <Z> on all qubits
estimator = Estimator(options=options)
job = estimator.run([pub_x, pub_y, pub_z])
jobs_train.append(job)
Training data progress: 100%|██████████| 172/172 [13:03<00:00, 4.55s/it]
if run_experiment:
for i in tqdm.tqdm(
range(len(train_data)), desc="Retrieving training data results"
):
# Completed job
job = jobs_train[i]
# Job results
job_result_x = job.result()[0].data.evs
job_result_y = job.result()[1].data.evs
job_result_z = job.result()[2].data.evs
# Record <X>, <Y> and <Z> on all qubits for the current datapoint
projections_train.append([job_result_x, job_result_y, job_result_z])
نكرر ذلك على مجموعة الاختبار.
# Identity operator on all qubits
id = "I" * num_qubits
# projections_test[i][j][k] will be the expectation value of the j-th Pauli operator (0: X, 1: Y, 2: Z)
# of datapoint i on qubit k
projections_test = []
jobs_test = []
# Experiment options for error mitigation
num_randomizations = 300
shots_per_randomization = 100
noise_factors = [1, 3, 5]
experimental_opts = {}
experimental_opts["resilience"] = {
"measure_mitigation": True,
"zne_mitigation": True,
"zne": {
"noise_factors": noise_factors,
"amplifier": "gate_folding",
"return_all_extrapolated": True,
"return_unextrapolated": True,
"extrapolated_noise_factors": [0] + noise_factors,
},
}
experimental_opts["twirling"] = {
"num_randomizations": num_randomizations,
"shots_per_randomization": shots_per_randomization,
"strategy": "active-accum",
}
options = EstimatorOptions(experimental=experimental_opts)
if run_experiment:
with Batch(backend=backend):
for i in tqdm.tqdm(range(len(test_data)), desc="Test data progress"):
# Get test sample
parameters = test_data[i]
# Bind parameter to the circuit and simplify it
qc_bound = qc.assign_parameters(parameters)
transpiler = generate_preset_pass_manager(
optimization_level=3, basis_gates=["u3", "cz"]
)
transpiled_circuit = transpiler.run(qc_bound)
# Transpile for hardware
transpiler = generate_preset_pass_manager(
optimization_level=3, target=target
)
transpiled_circuit = transpiler.run(transpiled_circuit)
# We group all commuting observables
# These groups are the Pauli X, Y and Z operators on individual qubits
observables_x = [
SparsePauliOp(id[:i] + "X" + id[(i + 1) :]).apply_layout(
transpiled_circuit.layout
)
for i in range(num_qubits)
]
observables_y = [
SparsePauliOp(id[:i] + "Y" + id[(i + 1) :]).apply_layout(
transpiled_circuit.layout
)
for i in range(num_qubits)
]
observables_z = [
SparsePauliOp(id[:i] + "Z" + id[(i + 1) :]).apply_layout(
transpiled_circuit.layout
)
for i in range(num_qubits)
]
# We define the primitive unified blocs (PUBs) consisting of the embedding circuit,
# set of observables and the circuit parameters
pub_x = (transpiled_circuit, observables_x)
pub_y = (transpiled_circuit, observables_y)
pub_z = (transpiled_circuit, observables_z)
# We define and run the estimator to obtain <X>, <Y> and <Z> on all qubits
estimator = Estimator(options=options)
job = estimator.run([pub_x, pub_y, pub_z])
jobs_test.append(job)
Test data progress: 100%|██████████| 74/74 [00:13<00:00, 5.56it/s]
يمكننا استخراج النتائج كما فعلنا سابقاً.
if run_experiment:
for i in tqdm.tqdm(
range(len(test_data)), desc="Retrieving test data results"
):
# Completed job
job = jobs_test[i]
# Job results
job_result_x = job.result()[0].data.evs
job_result_y = job.result()[1].data.evs
job_result_z = job.result()[2].data.evs
# Record <X>, <Y> and <Z> on all qubits for the current datapoint
projections_test.append([job_result_x, job_result_y, job_result_z])
الخطوة 4: المعالجة اللاحقة وإرجاع النتيجة بالتنسيق الكلاسيكي المطلوب
تعريف نواة الكم المسقطة
تُعرَّف نواة الكم المسقطة بدالة النواة التالية:
في المعادلة أعلاه، هو معامل فرط المعلمات القابل للضبط. وتُشكِّل عناصر مصفوفة النواة .
باستخدام تعريف 1-RDMs، يمكننا رؤية أن الحدود الفردية داخل دالة النواة يمكن تقييمها كـ ، حيث . هذه القيم المتوقعة هي تماماً ما قسناه أعلاه.
باستخدام scikit-learn، يمكننا في الواقع حساب النواة بسهولة أكبر. يعود ذلك إلى توفر دالة القاعدة الشعاعية ('rbf') جاهزة: . أولاً، نحتاج فقط إلى إعادة تشكيل مجموعتَي بيانات التدريب والاختبار المُسقَطتَين الجديدتَين إلى مصفوفات ثنائية الأبعاد.
لاحظ أن المرور على المجموعة بأكملها قد يستغرق نحو 80 دقيقة على وحدة المعالجة الكمومية. ولضمان إمكانية تنفيذ بقية الدرس بسهولة، نُوفِّر أيضاً إسقاطات من تجربة سابقة (مضمّنة في الملفات التي نزّلتها في خلية كود Download dataset). إذا أجريت التدريب بنفسك، يمكنك الاستمرار في الدرس بنتائجك الخاصة.
if run_experiment:
projections_train = np.array(projections_train).reshape(
len(projections_train), -1
)
projections_test = np.array(projections_test).reshape(
len(projections_test), -1
)
else:
projections_train = np.loadtxt("projections_train.txt")
projections_test = np.loadtxt("projections_test.txt")
آلة المتجهات الداعمة (SVM)
يمكننا الآن تشغيل SVM كلاسيكية على هذه النواة المُحسَبة مسبقاً، واستخدام النواة بين مجموعتَي الاختبار والتدريب للتنبؤ.
# Range of 'C' and 'gamma' values as SVC hyperparameters
C_range = [0.001, 0.005, 0.007]
C_range.extend([x * 0.01 for x in range(1, 11)])
C_range.extend([x * 0.25 for x in range(1, 60)])
C_range.extend(
[
20,
50,
100,
200,
500,
700,
1000,
1100,
1200,
1300,
1400,
1500,
1700,
2000,
]
)
gamma_range = ["auto", "scale", 0.001, 0.005, 0.007]
gamma_range.extend([x * 0.01 for x in range(1, 11)])
gamma_range.extend([x * 0.25 for x in range(1, 60)])
gamma_range.extend([20, 50, 100])
param_grid = dict(C=C_range, gamma=gamma_range)
# Support vector classifier
svc = SVC(kernel="rbf")
# Define the cross validation
cv = StratifiedKFold(n_splits=10)
# Grid search for hyperparameter tuning (q: quantum)
grid_search_q = GridSearchCV(
svc, param_grid, cv=cv, verbose=1, n_jobs=-1, scoring="f1_weighted"
)
grid_search_q.fit(projections_train, train_labels)
# Best model with best parameters
best_svc_q = grid_search_q.best_estimator_
print(
f"The best parameters are {grid_search_q.best_params_} with a score of {grid_search_q.best_score_:.4f}"
)
# Test accuracy
accuracy_q = best_svc_q.score(projections_test, test_labels)
print(f"Test accuracy with best model: {accuracy_q:.4f}")
Fitting 10 folds for each of 6622 candidates, totalling 66220 fits
The best parameters are {'C': 8.5, 'gamma': 0.01} with a score of 0.6980
Test accuracy with best model: 0.8108
المقارنة المرجعية الكلاسيكية
يمكننا تشغيل SVM كلاسيكية مع دالة القاعدة الشعاعية كنواة دون إجراء إسقاط كمي. تُمثِّل هذه النتيجة المعيار الكلاسيكي لدينا.
# Support vector classifier
svc = SVC(kernel="rbf")
# Grid search for hyperparameter tuning (c: classical)
grid_search_c = GridSearchCV(
svc, param_grid, cv=cv, verbose=1, n_jobs=-1, scoring="f1_weighted"
)
grid_search_c.fit(train_data, train_labels)
# Best model with best parameters
best_svc_c = grid_search_c.best_estimator_
print(
f"The best parameters are {grid_search_c.best_params_} with a score of {grid_search_c.best_score_:.4f}"
)
# Test accuracy
accuracy_c = best_svc_c.score(test_data, test_labels)
print(f"Test accuracy with best model: {accuracy_c:.4f}")
Fitting 10 folds for each of 6622 candidates, totalling 66220 fits
The best parameters are {'C': 10.75, 'gamma': 0.04} with a score of 0.7830
Test accuracy with best model: 0.7432
الملحق: التحقق من إمكانية تحقيق ميزة كمية للمجموعة في مهام التعلم
لا توفر جميع المجموعات ميزة محتملة من استخدام PQKs. ثمة بعض الحدو�د النظرية التي يمكن استخدامها كاختبار أولي لمعرفة ما إذا كانت مجموعة بيانات معينة يمكن الاستفادة من PQKs. لقياس ذلك، يُعرِّف مؤلفو قوة البيانات في التعلم الآلي الكمي [2] كميات يُشار إليها بتعقيدات النموذج الكلاسيكي والكمي والفصل الهندسي للنموذجين الكلاسيكي والكمي. لتوقع ميزة كمية محتملة من PQKs، ينبغي أن يكون الفصل الهندسي بين النواتَين الكلاسيكية والكمية المسقطة تقريباً في حدود ، حيث هو عدد عينات التدريب. إذا تحقق هذا الشرط، ننتقل إلى التحقق من تعقيدات النموذج. إذا كان تعقيد النموذج الكلاسيكي في حدود بينما تعقيد النموذج الكمي المسقط أصغر بكثير من ، يمكننا توقع ميزة محتملة م�ن PQK. يُعرَّف الفصل الهندسي على النحو التالي (F19 في [2]):
# Gamma values used in best models above
gamma_c = grid_search_c.best_params_["gamma"]
gamma_q = grid_search_q.best_params_["gamma"]
# Regularization parameter used in the best classical model above
C_c = grid_search_c.best_params_["C"]
l_c = 1 / C_c
# Classical and quantum kernels used above
K_c = rbf_kernel(train_data, train_data, gamma=gamma_c)
K_q = rbf_kernel(projections_train, projections_train, gamma=gamma_q)
# Intermediate matrices in the equation
K_c_sqrt = sqrtm(K_c)
K_q_sqrt = sqrtm(K_q)
K_c_inv = inv(K_c + l_c * np.eye(K_c.shape[0]))
K_multiplication = (
K_q_sqrt @ K_c_sqrt @ K_c_inv @ K_c_inv @ K_c_sqrt @ K_q_sqrt
)
# Geometric separation
norm = np.linalg.norm(K_multiplication, ord=np.inf)
g_cq = np.sqrt(norm)
print(
f"Geometric separation between classical and quantum kernels is {g_cq:.4f}"
)
print(np.sqrt(len(train_data)))
Geometric separation between classical and quantum kernels is 1.5440
13.114877048604
يُعرَّف تعقيد النموذج على النحو التالي (M1 في [2]):
# Model complexity of the classical kernel
# Number of training data
N = len(train_data)
# Predicted labels
pred_labels = best_svc_c.predict(train_data)
pred_matrix = np.outer(pred_labels, pred_labels)
# Intermediate terms
K_c_inv = inv(K_c + l_c * np.eye(K_c.shape[0]))
# First term
first_sum = np.sum((K_c_inv @ K_c_inv) * pred_matrix)
first_term = l_c * np.sqrt(first_sum / N)
# Second term
second_sum = np.sum((K_c_inv @ K_c @ K_c_inv) * pred_matrix)
second_term = np.sqrt(second_sum / N)
# Model complexity
s_c = first_term + second_term
print(f"Classical model complexity is {s_c:.4f}")
Classical model complexity is 1.3578
# Model complexity of the projected quantum kernel
# Number of training data
N = len(projections_train)
# Predicted labels
pred_labels = best_svc_q.predict(projections_train)
pred_matrix = np.outer(pred_labels, pred_labels)
# Regularization parameter used in the best classical model above
C_q = grid_search_q.best_params_["C"]
l_q = 1 / C_q
# Intermediate terms
K_q_inv = inv(K_q + l_q * np.eye(K_q.shape[0]))
# First term
first_sum = np.sum((K_q_inv @ K_q_inv) * pred_matrix)
first_term = l_q * np.sqrt(first_sum / N)
# Second term
second_sum = np.sum((K_q_inv @ K_q @ K_q_inv) * pred_matrix)
second_term = np.sqrt(second_sum / N)
# Model complexity
s_q = first_term + second_term
print(f"Quantum model complexity is {s_q:.4f}")
Quantum model complexity is 1.5806
المراجع
- Utro, Filippo, et al. "Enhanced Prediction of CAR T-Cell Cytotoxicity with Quantum-Kernel Methods." arXiv preprint arXiv:2507.22710 (2025).
- Huang, Hsin-Yuan, et al. "Power of data in quantum machine learning." Nature communications 12.1 (2021): 2631.
- Daniels, Kyle G., et al. "Decoding CAR T cell phenotype using combinatorial signaling motif libraries and machine learning." Science 378.6625 (2022): 1194-1200.